ゲノムの時代へ
膨大な情報を、
わたしたちは自在にあやつって、
新しい時代を拓くことができるのか、
やがてくる明日への羅針盤に
長く、直に読む技術へ シークエンサーの進歩
図を拡大
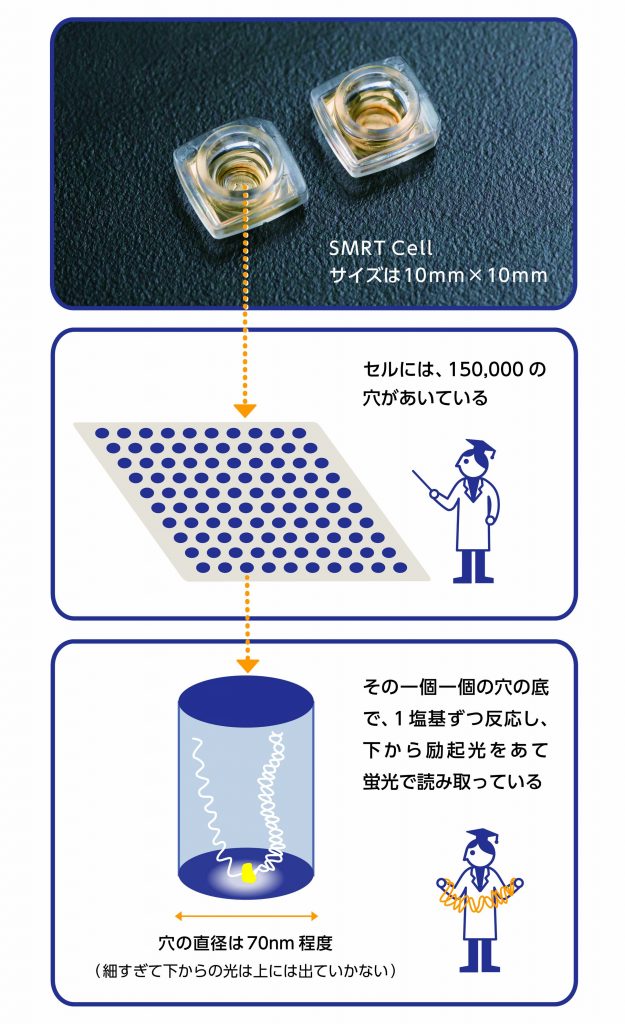 DNAの配列を解読する技術は、ここ十数年の間に驚異的な進歩を遂げました。昔は、サンガーシークエンス※1という方法で、DNAの断片を1本1本調べていましたが、次世代シークエンサーの登場により、数億から数十億本のDNA断片を一度に調べることが可能となりました。これにより、一昔前はヒト一人分のDNA配列を調べるのに10年以上かかりましたが、今はおよそ2日間で終わります。
DNAの配列を解読する技術は、ここ十数年の間に驚異的な進歩を遂げました。昔は、サンガーシークエンス※1という方法で、DNAの断片を1本1本調べていましたが、次世代シークエンサーの登場により、数億から数十億本のDNA断片を一度に調べることが可能となりました。これにより、一昔前はヒト一人分のDNA配列を調べるのに10年以上かかりましたが、今はおよそ2日間で終わります。
現在、主流の次世代シークエンサーは、蛍光色素を用いてDNA配列を解読しています。しかし、蛍光色素の検出感度が低いため、解析するDNA断片を増幅※2しなくてはならず、増幅しにくい部分の解析ができません。また、連続して200文字 (塩基) 程度しか読みとることができないため※3、ヒトゲノムで同じような配列が繰り返された場所などは、解読が困難です。
そんな中、全く異なる原理の「一分子長鎖シークエンサー」が注目されています。このシークエンサーも、蛍光色素を用いてDNA配列を解読しますが、検出感度が高いため、1分子 (1本) のDNAをそのまま、増幅することなく解析できます。また、連続して1万塩基以上読みとることができます。ただし、この一分子長鎖シークエンサー、まだ解析コストと解析にかかる時間の点で、多くの方のゲノムDNAを解読するのには適していません。しかし、ヒトゲノムの複雑な領域の解析に大きな威力を発揮するため、今後のさらに活用されていくものと思われます。最近では、蛍光色素を使わないで、直にDNA配列を解読する一分子長鎖シークエンサーも登場しました。蛍光の検出器がいらないため、シークエンサーを驚くほど小型化できるようです※4。今後も、「より長く、正確に、短時間で」DNA配列の解読技術は、更なる発展を遂げていくことでしょう。
【参考】
※1 サンガーシークエンス: フレデリック・サンガー博士が発明したDNA塩基の決定方法で、ジデオキシ法とも呼ばれる。サンガー博士はこの発明で1980年にノーベル化学賞を受賞しています。
※2 増幅: ポリメラーゼ連鎖反応 (PCR)と呼ぶ方法で行います。1本のDNAからその複製を作り、さらにその複製を作り、この反応を繰り返し、1000本程度に増やします。
※3 1000本に増やしたDNAが二人三脚ならぬ、千人千一脚をしていると想像してください。走り始めは、みんな息も揃っていますが、そのうち、早く走る人、遅く走る人とバラバラになって、しまいには走れなくなりますよね。それと同じイメージです。丁度200歩ぐらいで、反応がバラバラになってしまうのです。
※4 最近試験的に売りだされた次世代シークエンサーは、USBのメモリスティック程度の大きさで、実際にパソコンのUSBに挿して使用するものもあります。
【関連リンク】
日本人の基準ゲノム配列(JRG)を公開
最新記事一覧
-
- きこえと遺伝子医療の現在
- 2025.12.26|宇佐美真一
-
- 人体を取りまく常在菌〜機能を知って共存しよう〜
- 2020.12.16|後藤まき
-
- なぜウイルスははやく変化するのか?
- 2020.09.08|山口由美
-
- 棒状で増やすか環状で増やすか―新たなシークエンサー開発―
- 2020.07.16|川嶋順子
-
- 新型コロナウイルスに対する抗体
- 2020.05.18|峯岸直子
